藥用蘑菇樟芝(異名牛樟芝、牛樟芝)的有性雜交、染色體水平基因組序列及比較基因組分析
摘要
台灣香樟蘑菇是宿醉、癌症、高血壓、肥胖、糖尿病和發炎的補充和替代藥物。儘管台灣樟芝已引起生物技術和藥理學的廣泛關注,但經典的遺傳學或基因組方法尚未對其建立適當的方法。我們從兩個 T 中分離出了四個有性能力的單核體。樟腦雙核分別用於橙紅色(HC1)和乳白色(SN1)蘑菇的商業種植。我們也對這四種單核體的高品質染色體水平基因組序列進行了定序、註釋和比較分析。這些基因組資源為了解這種經濟上重要的蘑菇的生物學、演化和次級代謝物生物合成提供了寶貴的基礎。我們證明T.樟樹具有四極交配系統,HC1和SN1代表兩個表現出核型變異的種內分離株。與幾種食用菌模式生物相比,T.樟樹的基因家族和個體基因數量顯著收縮,尤其是植物、真菌和細菌細胞壁降解酶,這解釋了為什麼樟樹。香樟菇在自然環境中很少見,人工栽培難度較高、耗時長,且易受真菌和細菌感染。我們的結果為深入的T奠定了基礎。樟樹研究,包括精確的基因操作、蘑菇結果的改進以及生產天然藥用產品的合成生物學應用。 重要性台灣樟腦真菌(Tc)是一種擔子菌,會引起芳香樹肉桂褐心腐病。 Tc子實體首先被台灣原住民用來治療宿醉、腹痛、腹瀉、高血壓等疾病,後來被許多國家的人們用來治療宿醉、腹痛、腹瀉、高血壓等疾病。為了建立這種經濟上重要的藥用蘑菇的經典遺傳和基因組方法,我們首先從廣泛用於 Tc 蘑菇商業生產的兩個雙核體中分離和表徵了四個有性能力的單核體。我們應用 PacBio 單分子即時定序技術來確定四個單核體的接近完整的基因組序列。這些端粒到端粒和無間隙單倍體基因組序列揭示了所有需要研究和發現的基因組變異,包括著絲粒、端粒、逆轉錄轉座子、交配型基因座、生物合成和代謝基因簇。 Tc 和其他幾種蘑菇模式生物之間也發現了顯著的種間多樣性,包括Agrocybe aegerita、Coprinopsis cinerea、Schizophyllum commune 和Ganoderma lucidum。 img src=" /zb_users/upload/2024/12/spectrum.02032-21-f001.jpg" alt="FIG 1" />
圖1
樟腦的形態特徵…
圖1
樟腦營養菌絲體和子實體的形態特徵。 (A 到 J)…
圖 1 樟腦營養菌絲體和子實體的形態特徵。 (A 到 J) 營養雙核和單核培養物的菌落形態和顏色。 (K 到 P) 三種代表性樟腦蘑菇表面的冷凍掃描電子顯微鏡影像。只有W1×W2和V5×V7(但不是W1×V7)蘑菇顯示出一些帶有四個擔子孢子的擔子。比例尺 = 0.04 毫米。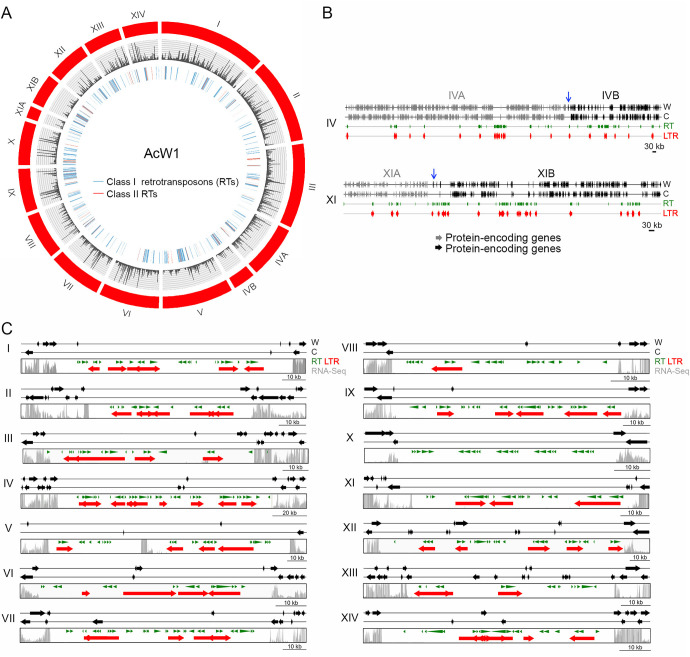
圖 2
< p> 14 條W1 染色體和...圖2
14 條W1 染色體及其著絲粒。 (A) 14 W1 的可視化…
圖 2 14 W1 染色體及其著絲粒。 (A) 使用 CIRCOS (http://circos.ca) 對 14 條 W1 染色體進行可視化。外圈表示W1的所有染色體和超級支架(紅色)。中間的圓圈是 RNA-seq 讀取深度的圖。 I 類 RT(藍色)和 II 類 RT(紅色)顯示在內部跡線中。 (B) 分別說明 ChIVA(灰色)和 ChIVB(黑色)之間以及 ChXIA(灰色)和 ChXIB(黑色)之間重疊區域的示意圖。重疊區域由藍色箭頭指示。 (C) 14 個假定的 W1 著絲粒區域的示意圖。這些間隔被定義為相應染色體上最長的無 ORF 區域,並且大部分包含 RT。 RNA定序分析表明,相對於側翼非著絲粒區域,所鑑定的著絲粒區域的轉錄活性水平也降低。灰色條表示 RNA-seq 讀取深度。由RepeatMasker搜尋程式(http://www.repeatmasker.org/)(8)和LTR-finder程式(http://tlife.fudan.edu.cn/tlife/ltr_finder/)(12)預測的RT為分別用綠色和紅色表示。表 S8 列出了所有 14 個 W1 著絲粒的位置。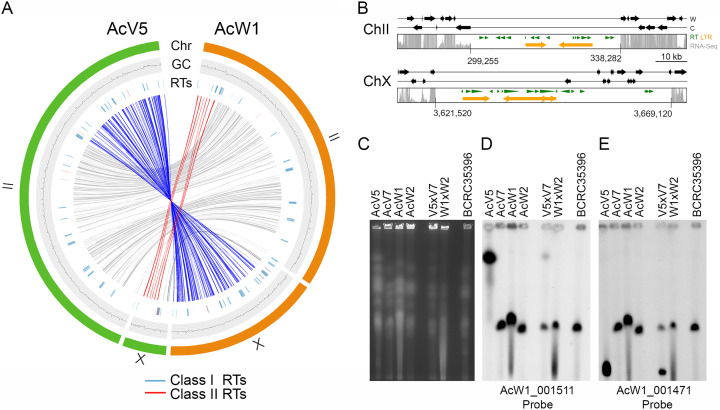
圖 3
< p> V5 中的染色體易位。 (A)…圖 3
V5 中的染色體易位。 (A) 共線性關係以紅色、藍色或…
圖 3 V5 中的染色體轉位。 (A) 共線性關係在內圈中分別以紅色、藍色或灰色表示。外圈代表 W1-ChII 和 W1-ChX(橘色),以及 V5-ChII 和 V5-ChX(綠色)。兩條染色體的 GC 含量(視窗大小 5,000 bp)顯示在中間的跡線。 I 類 RT(藍色)和 II 類 RT(紅色)顯示在內部跡線中。 (B) 示意圖說明 V5-ChII 和 V5-ChX 上的推定著絲粒區域。灰色條表示 RNA-seq 讀取深度。由RepeatMasker搜尋程式(http://www.repeatmasker.org/)(8)和LTR-finder程式(http://tlife.fudan.edu.cn/tlife/ltr_finder/)(12)預測的RT為分別以綠色和橙色表示。標示了兩個 V5 著絲粒的位置。 (C) 應用 PFGE 分離 V5、V7、W1、W2、V5×V7、W1×W2 和 BCRC35396 的染色體。 (D 到 E) 用兩個 DNA 探針進行 Southern 雜交,如圖所示。這些結果為我們的 W1 和 V5 基因組組裝提供了額外的證據。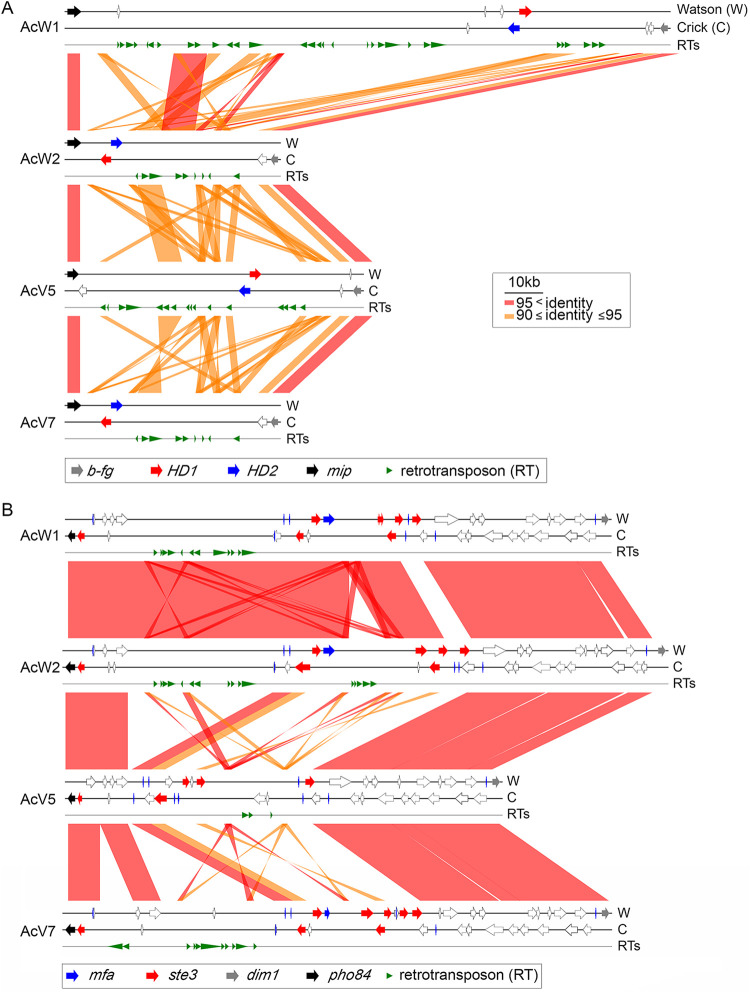
圖 4
< p> matA 交配周圍的同線性…圖4
matA 交配型基因座(A) 和matB 交配型基因座周圍的同線性…
圖4 matA 周圍的同線性W1、W2、V5 和 V7 的交配型基因座 (A) 和 matB 交配型基因座 (B)。兩條 DNA 鍊和逆轉錄轉座子分別表示為 Watson (W)、Crick (C) 和 RT。 RT 由 RepeatMasker 搜尋程式 (http://www.repeatmasker.org/) 預測 (8)。 HD1、HD2、b-fg、mip1、ste3、mfa、dim1 和 pho84 分別以紅色、藍色、灰色、黑色、紅色、藍色、灰色和黑色箭頭表示。其他蛋白質編碼基因由空心箭頭指示。
圖 5
< p> 候選樟腦果實相關基因(FRG) 和差異表達基因的比較轉錄組鑑定...圖5
候選樟樹結果相關基因(FRG) 和差異表達的比較轉錄組鑑定...
圖5 比較橙紅色樟樹菌株中候選樟樹結果相關基因(FRG)和差異表達基因(DEG)的轉錄組鑑定。 (A, B) VENN 圖顯示 8,289 個樟芝 W1 蛋白編碼基因在 C. cinerea 中至少有一個直向同源物。在這些蛋白質編碼基因中,254 個和 3,797 個胺基酸序列分別與 410 個灰黴病菌 FB 起始基因 (CcFBIG) 和 5,031 個灰黴病菌 FB 發育基因 (CcFBDG) 高度相似 (20)。 (C) 樟腦 W1 的 1,280 個 FRG 的 VENN 圖,其中 73 個和 560 個分別是 58 個 CcFBIG 和 489 個 CcFBDG 的直系同源物,另外 354 個是樟腦特異性的。此外,289 既不是 CcFBIG 的直系同源物,也不是 CcFBDG 的直系同源物。 (D) 樟腦 W1 中 3,835 個 lncRNA 的圓餅圖。有 188 個與果實相關的 lncRNA (FRLR) 和 278 個與營養菌絲相關的 lncRNA (VHLR)。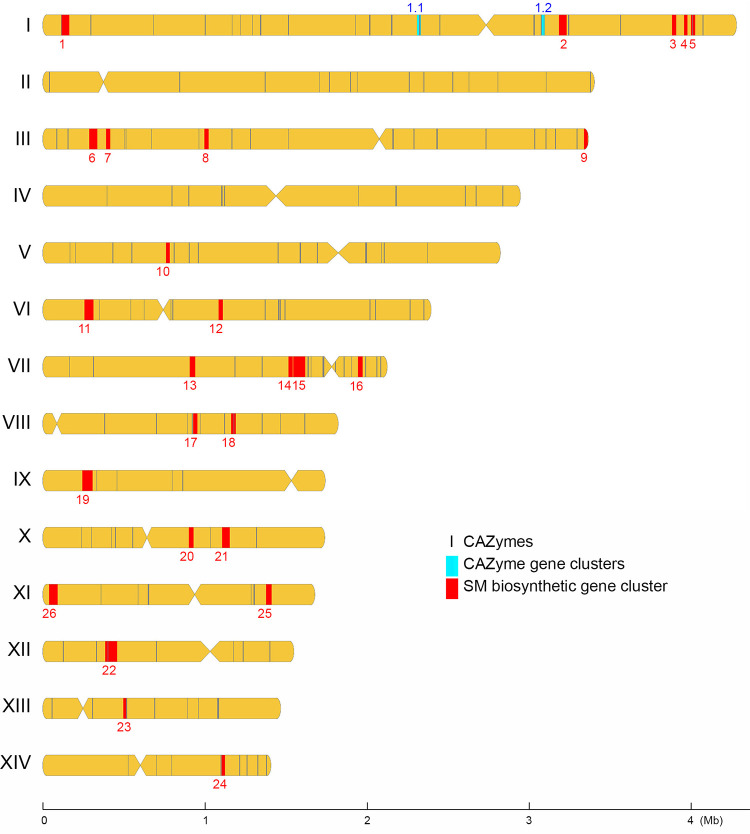
圖 6
< p> CAZyme 基因的染色體分佈,…圖6
CAZyme 基因、CAZ-GC 和SM-BGC 在樟腦W1 中的染色體分佈。著絲粒…
圖6 CAZyme 基因、CAZ-GC 和SM-BGC 在樟腦W1 中的染色體分佈。著絲粒位置以有限的寬度顯示。沿著序列選擇所有 CAZyme 基因作為位置標記。各個 CAZyme 基因、2 個 CAZyme 基因簇 (CAZ-GC) 和 26 個次級代謝物生物合成基因簇 (SM-BGC) 的位置分別以黑色、青色和紅色表示。